Rで多重比較補正!をする前の準備。
久しぶりにRを開いたらエラーが出るわ出るわ
初心者ながらネットをみてなんとか解決しました…
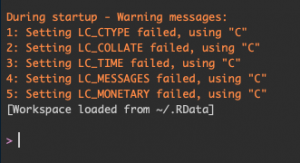
起動していきなりwarning。
ロケール設定をしてくださいとのこと。OSをアップデートしたためと思われます。
やり方はいくつかある様ですが、ターミナルを開いて(Rstudioはconsoleの隣にTerminalがあるから楽です)以下をコピペしてenter。日本語でラベルつけたい人は上を。ヘルプとかで変な日本語が出るくらいなら英語の方がいい人は下を。
$ defaults write org.R-project.R force.LANG ja_JP.UTF-8 $ defaults write org.R-project.R force.LANG en_US.UTF-8
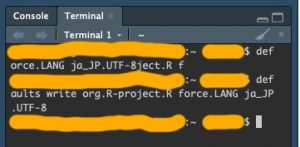
Rのコンソールからもできるみたいです
> system("defaults write org.R-project.R force.LANG ja_JP.UTF-8")
はいできた。Rを再起動してください。
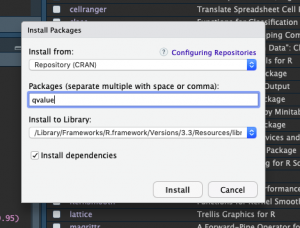
それでは今回の狙いのqvalueパッケージをさっそくインストール、できない…
Rを新しくして、Rstudioも新しくしてみたけどやっぱりダメ。
ggplot2が入ってないとか、でもなかった。足りないパッケージを一つずつインストールしようとしたけど、それもできず。
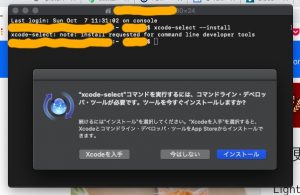
しばらく困った後最終的に判明したのは Xcode が古かった。
Terminalを開いて以下をコピペ。
$ xcode-select --install
なんやかんやしばらくかかって
できた。Rを再起動。
もう一つ
パッケージのインストール中に
unknown timezone ‘zone/tz/2017c.1.0/zoneinfo/Asia/Tokyo’ なるエラーが頻出。
これで止まることはなさそうですが、気持ちが悪い。
> Sys.setenv("TZ" = "Asia/Tokyo")
で消えました。アップデートで修正されると書いてあったらしいですが、まだ出ますね。
ようやく綺麗な初期画面になった。
qvalue.packageはRコンソールに以下をコピペでインストールが始まります。これが一番手っ取り早かった。
途中でyesとかallを選択しつつ待つこと数分
## try http:// if https:// URLs are not supported
source("https://bioconductor.org/biocLite.R")
biocLite("qvalue")
ついに、たどり着いたこの場面。
では解析を始めましょう To be continue…
 |
価格:2,916円 |
![]()



コメントを残す